东丽手机网站建设网络推广技术外包
1写在前面
最近在用的包经常涉及到SummarizedExperiment格式的文件,不知道大家有没有遇到过。🤒
一开始觉得这种格式真麻烦,后面搞懂了之后发现真是香啊,爱不释手!~😜
2什么是SummarizedExperiment
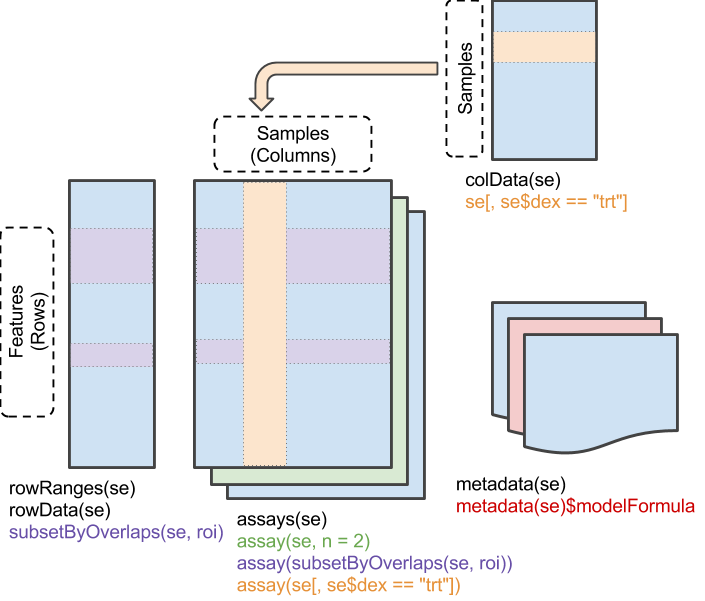
这种class主要包括了以下几个内容:👇
assay(), 包含一个或多个矩阵, 如行为基因名,列为样本;colData(), 对列的注释,格式为DataFrame, 如样本信息的描述;rowData()和(或)rowRanges(), 对列的注释,如rowRanges()描述基因坐标,rowData()描述每个基因差异分析后的logFC和pvalue;metadata(), 描述整个object的list;
3用到的包
rm(list = ls())
library(SummarizedExperiment)
library(tidyverse)
library(RColorBrewer)
library(airway)
library(edgeR)
4处理SummarizedExperiment对象
4.1 示例数据
这里我们用到airway包内的示例数据,讲解一下如何操作。🧐
这个data的基本研究设计是,用地塞米松处理人气道平滑肌细胞后进行RNA-seq。🤠
data(airway, package="airway")
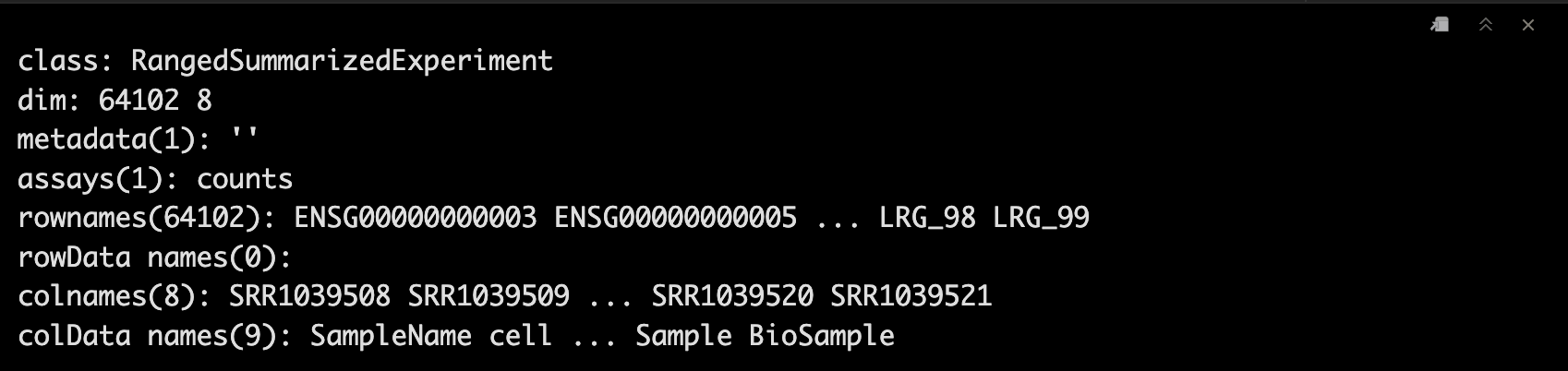
se <- airway
se
4.2 查看colData
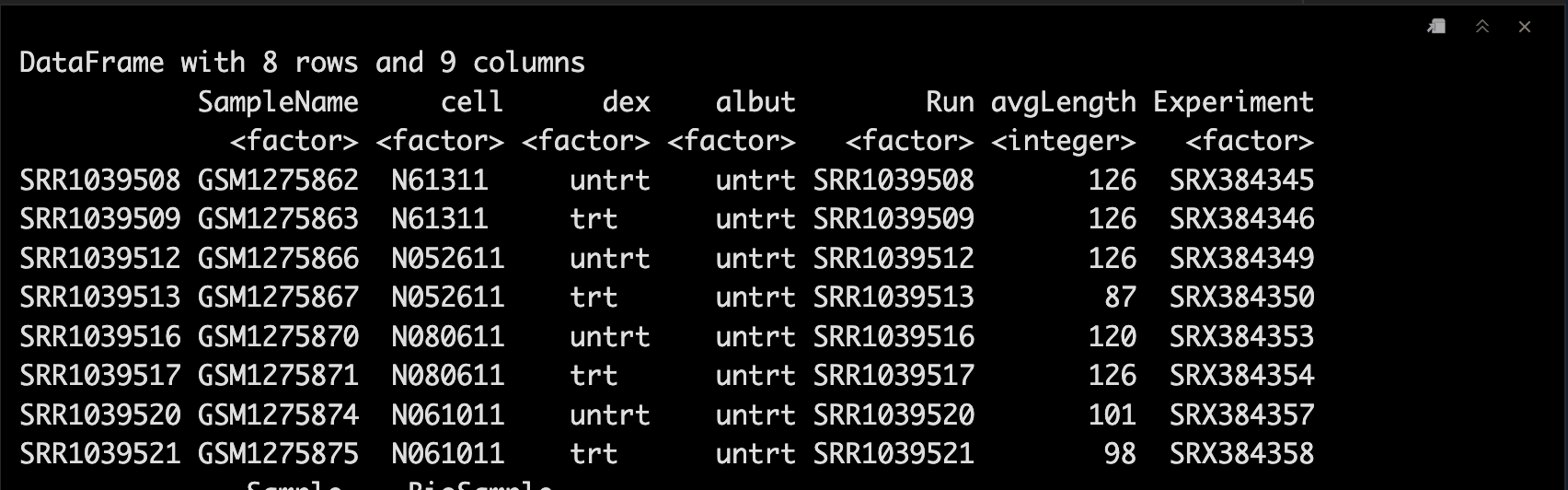
colData包含了样本或表型信息,返回的格式为DataFrame。🥰
colData(se)
4.3 提取colData的指定列
se$cell

4.4 查看列名和行名
我们看一下行名和列名。😉
colnames(se)

head(rownames(se))

4.5 查看表达矩阵名
assayNames(se)

4.6 查看表达矩阵
一个SummarizedExperiment格式的object是可以包含多个assay的。
assays(se)

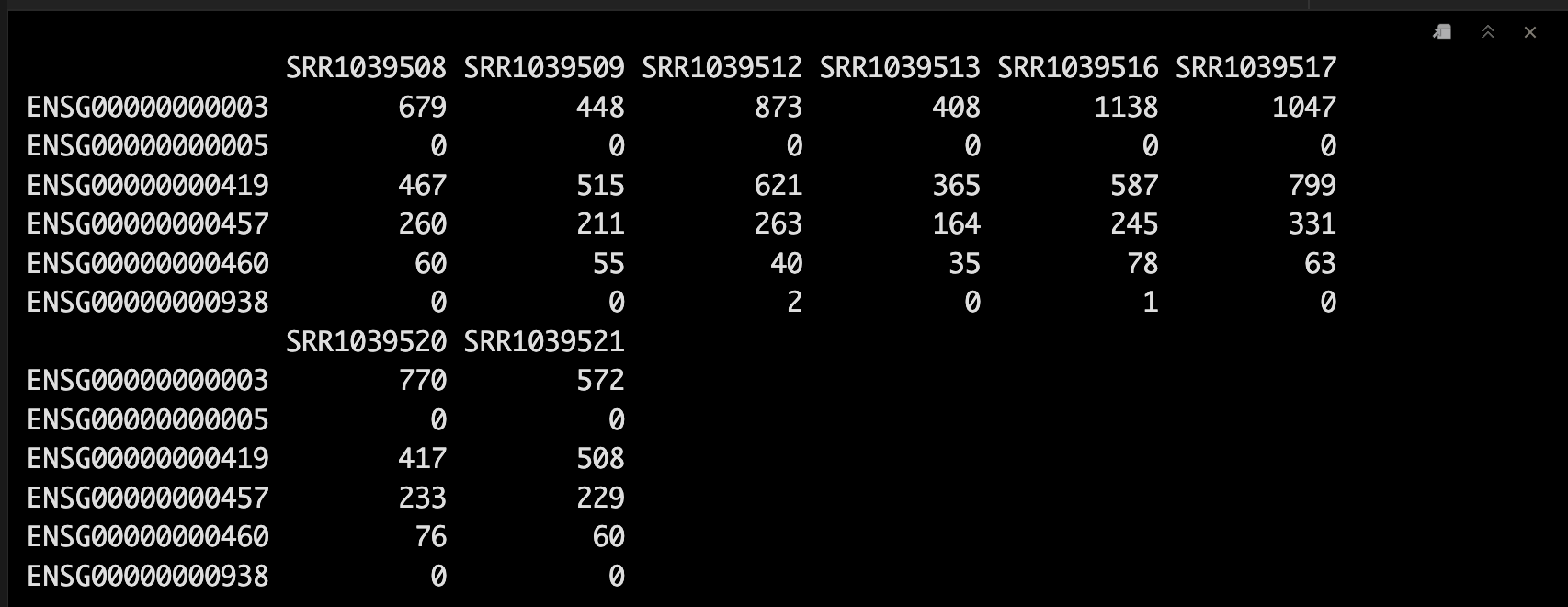
4.7 查看指定assay
head(assay(se, "counts"))
4.8 rowRanges或granges
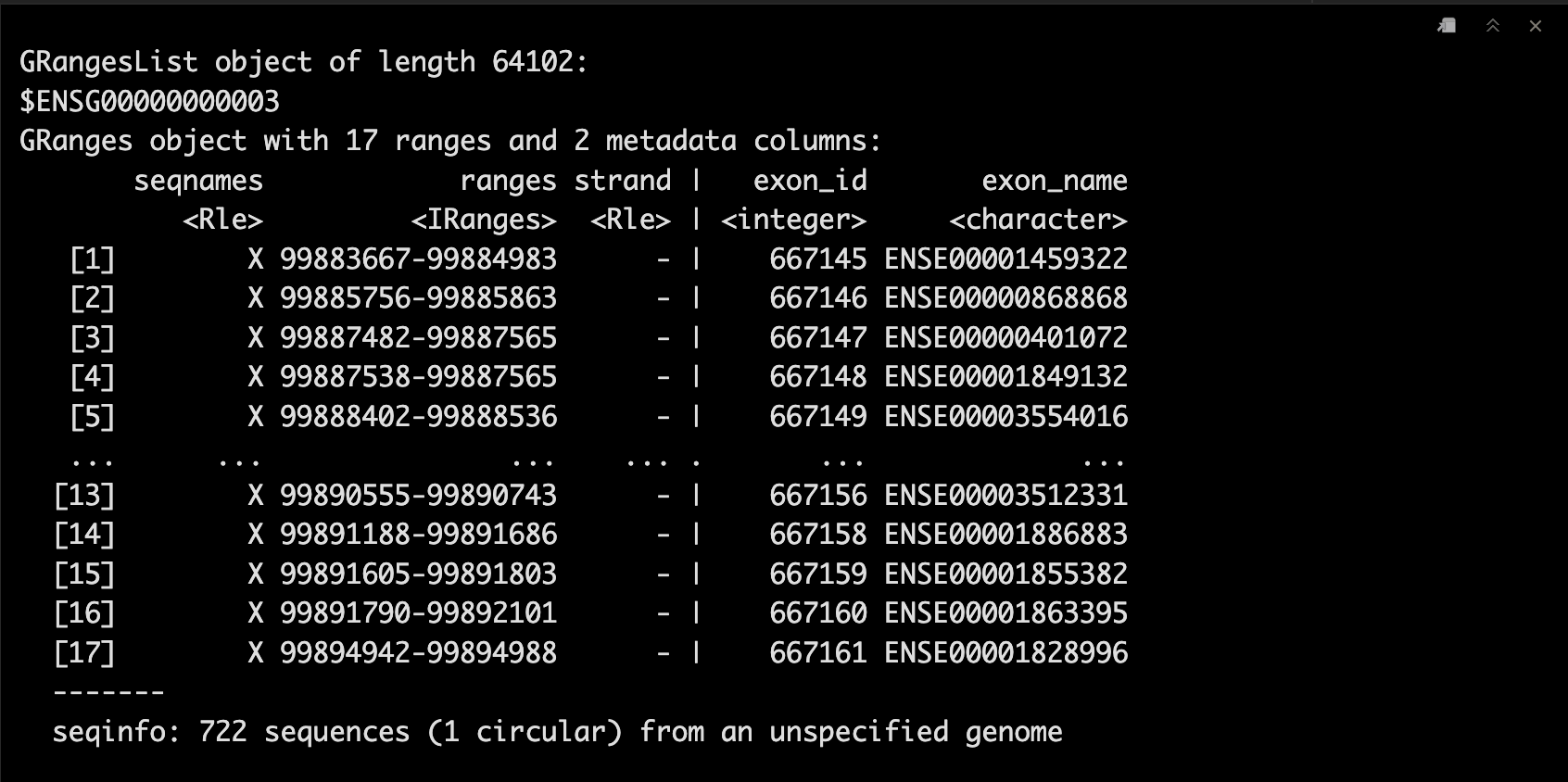
接下里是重中之重了,SummarizedExperiment允许代表不同特征的rowRanges (或granges)数据。🤩
length(rowRanges(se))

dim(se)

这里我们可以看到行特征对应了很多注释信息,这样我们在操作的时候就更加方便调取了。🤩
rowRanges(se)
4.9 获取start信息
start(rowRanges(se))
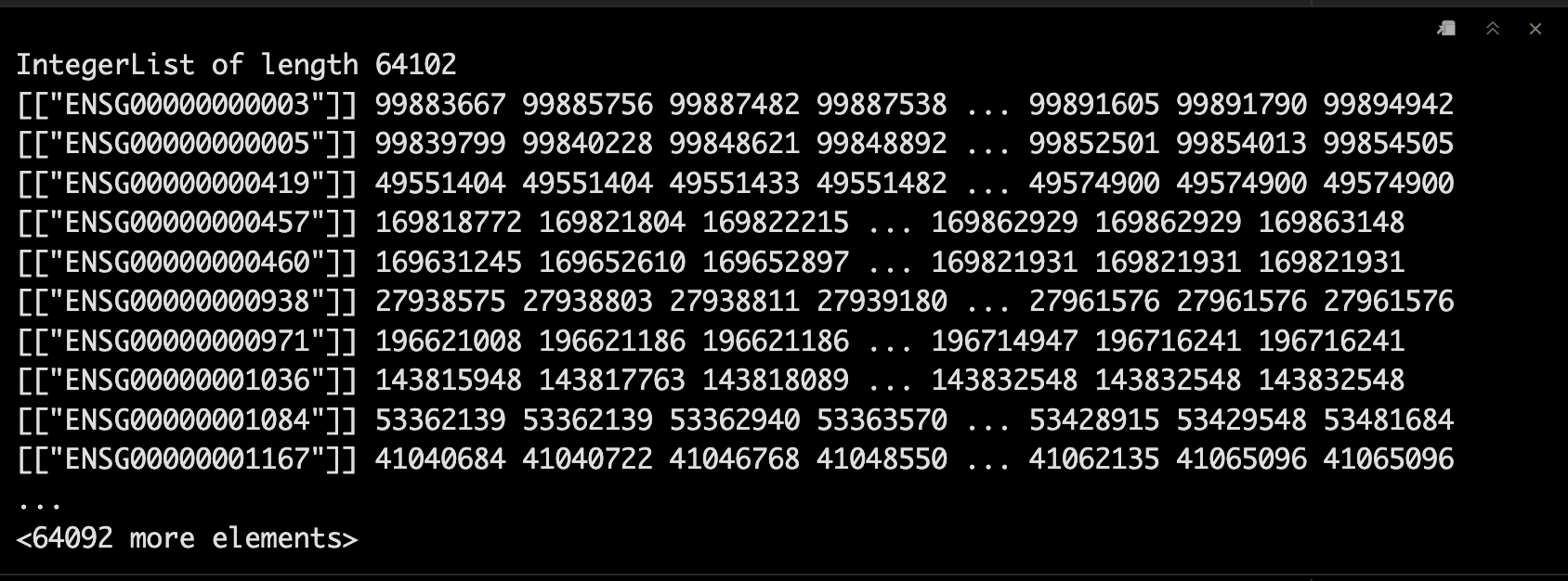
对于这种IRanges 对象, 你也可以直接使用start()函数获取,其他常见的函数还有end,width。🤩
start(se)
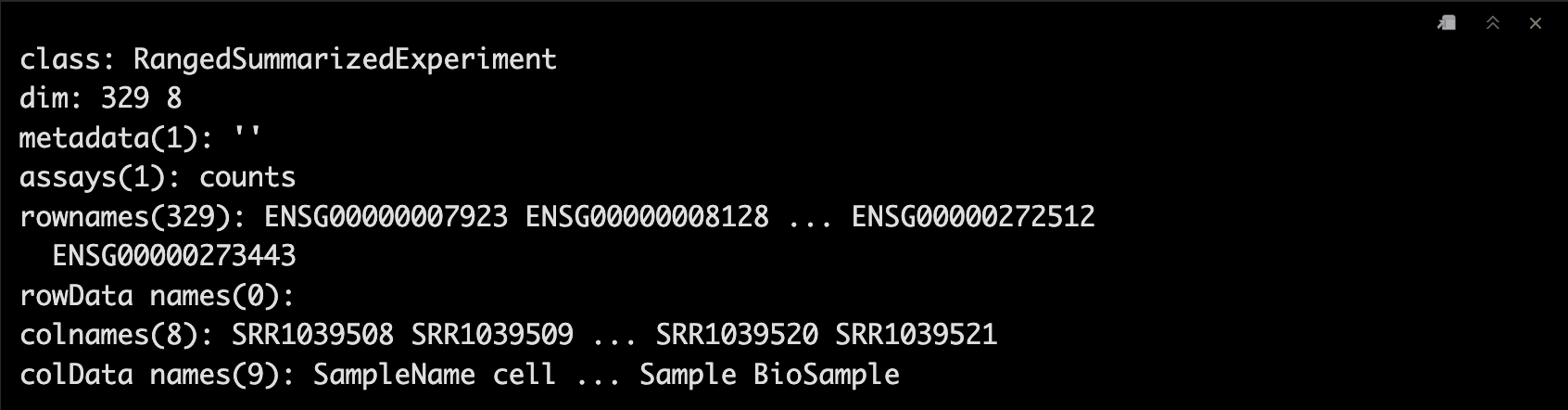
4.10 提取制定对象
如果我们只想获取制定条件下的SummarizedExperiment对象,可以用subsetByOverlaps()函数,或者直接使用GRanges[List]。🤓
gr <- GRanges(seqnames = "1", ranges = IRanges(start = 1, end = 10^7))
subsetByOverlaps(airway, gr)
5手动创建SummarizedExperiment
5.1 读入数据
这里我准备了样本数据和counts矩阵两个文件,大家跟着我一起试一下吧。
pdata <- read.csv("./SummarizedExperiment/airway-sample-sheet.csv")
counts <- read.csv("./SummarizedExperiment/airway-read-counts.csv")
5.2 整理数据并创建SummarizedExperiment
pdata <- column_to_rownames(pdata, "Run")
counts <- column_to_rownames(counts, "Run")
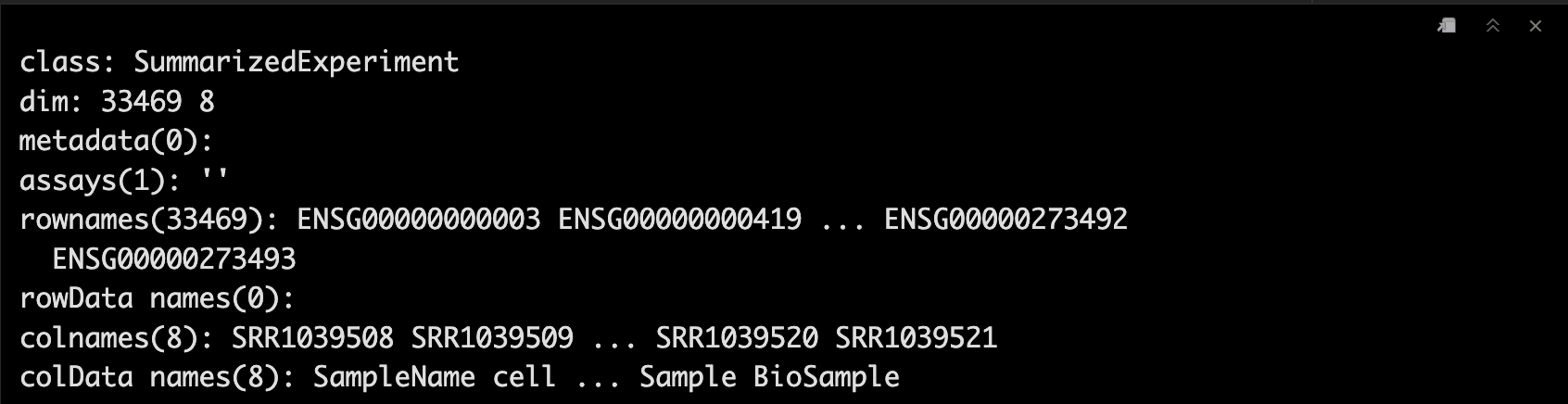
se_juan <- SummarizedExperiment(t(counts), colData = pdata, rowRanges = )
se_juan
5.3 准备rowData
我们再试着把rowData加进之前的SummarizedExperiment里。🤠
这里我们用一下EnsDb.Hsapiens.v86包来获取基因的各种信息,如染色体位置、起止位点、类型、id等等,这个包以后我们再具体讲怎么用。
输出的文件为Granges,完美匹配。😁
library(EnsDb.Hsapiens.v86)
edb <- EnsDb.Hsapiens.v86
filter <- rownames(se_juan)
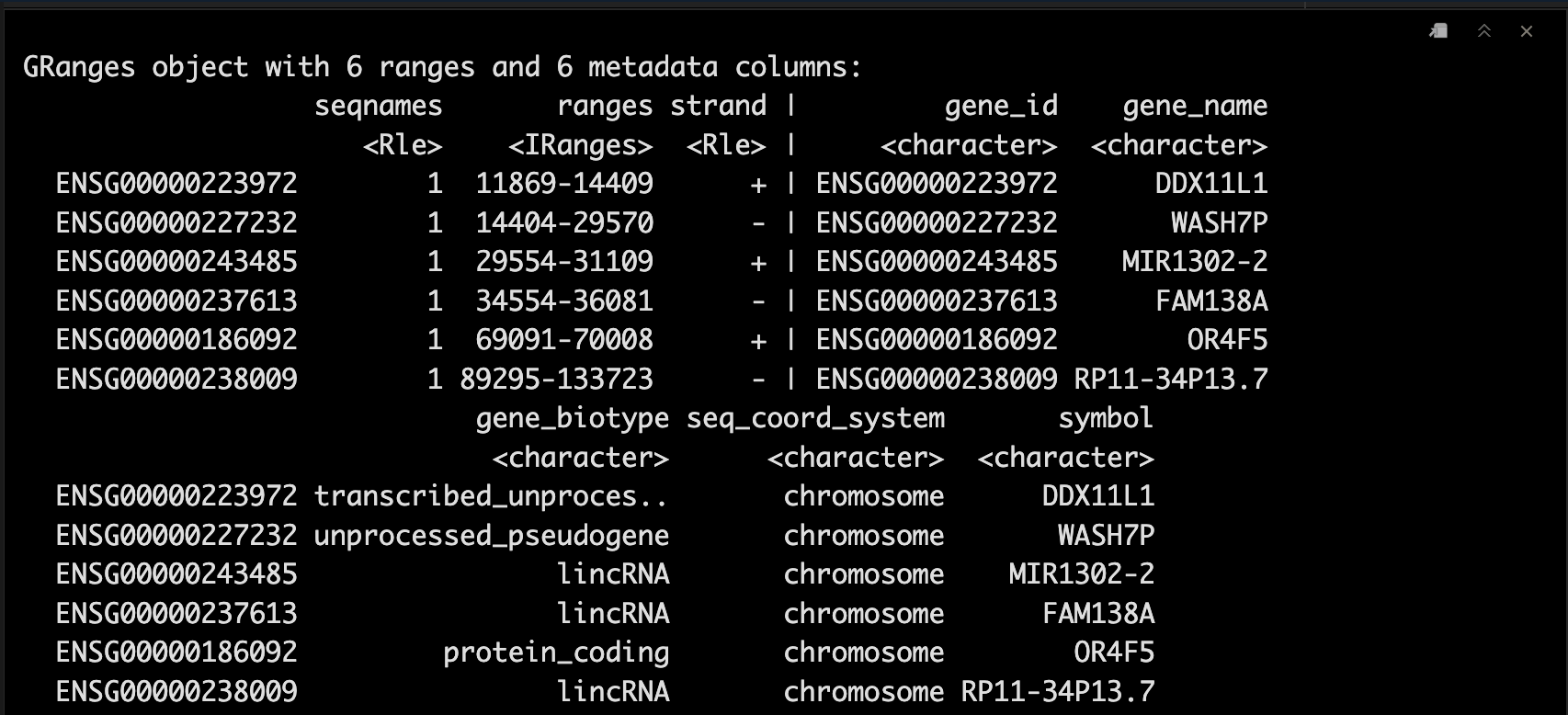
genes <- genes(edb)
genes <- genes[genes$gene_id %in% filter]
head(genes)
5.4 添加rowData
这里需要说一下,有的基因没有具体的位点信息等,可能和版本有关系,以后我们再讲怎么处理。🥰
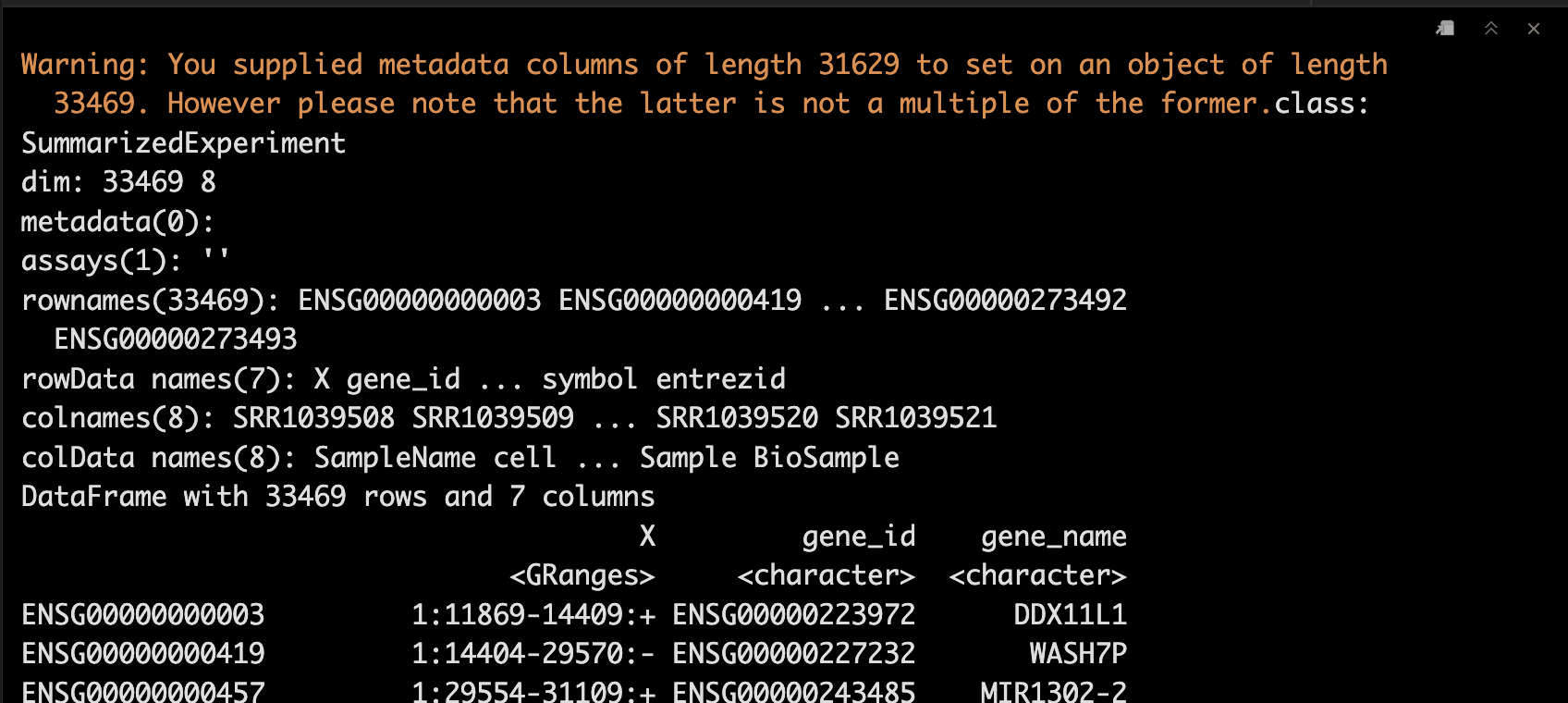
rowData(se_juan) <- genes
se_juan
rowData(se_juan)
6小练习
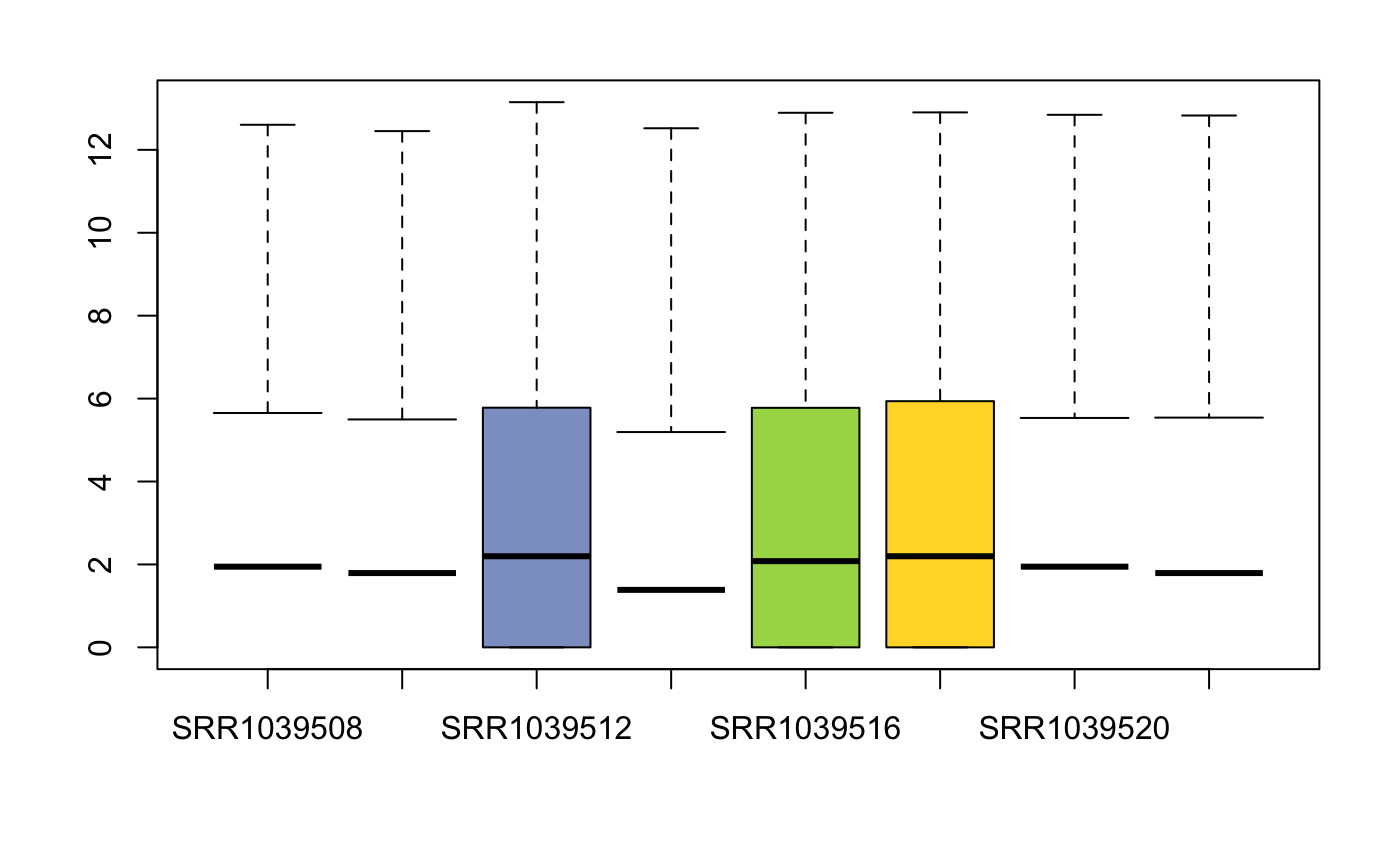
我们做个小练习,试试画个基因平均表达的boxplot吧, 还要取一下log哦。😏
assay(se_juan) %>%
log() %>%
boxplot(col = colorRampPalette(brewer.pal(8, "Set2"))(8))

需要示例数据的小伙伴,在公众号回复
SummarizedExperiment获取吧!点个在看吧各位~ ✐.ɴɪᴄᴇ ᴅᴀʏ 〰
📍 🤩 WGCNA | 值得你深入学习的生信分析方法!~
📍 🤩 ComplexHeatmap | 颜狗写的高颜值热图代码!
📍 🤥 ComplexHeatmap | 你的热图注释还挤在一起看不清吗!?
📍 🤨 Google | 谷歌翻译崩了我们怎么办!?(附完美解决方案)
📍 🤩 scRNA-seq | 吐血整理的单细胞入门教程
📍 🤣 NetworkD3 | 让我们一起画个动态的桑基图吧~
📍 🤩 RColorBrewer | 再多的配色也能轻松搞定!~
📍 🧐 rms | 批量完成你的线性回归
📍 🤩 CMplot | 完美复刻Nature上的曼哈顿图
📍 🤠 Network | 高颜值动态网络可视化工具
📍 🤗 boxjitter | 完美复刻Nature上的高颜值统计图
📍 🤫 linkET | 完美解决ggcor安装失败方案(附教程)
📍 ......
本文由 mdnice 多平台发布
